Capítulo 11 Partial Least Squares
Partial Least Squares (PLS) é um método que explora padrões de covariação entre dois ou mais blocos de variáveis. De modo similar à PCA/CVA, a PLS cria eixos ortogonais que, neste caso, explicam a covariância entre blocos. Em análises de MG, um dos blocos normalmente é a forma. O(s) bloco(s) adicional pode ser composto, por exemplo, por um grupo de variáveis climáticas, geográficas e/ou bióticas ou por outros descritores fenotípicos. Além disso, as variáveis dentro dos blocos não precisam ser independentes uma da outra, e o número de variáveis pode exceder o número de observações. Os blocos de variáveis podem conter variáveis de diversas naturezas (contínuas, categóricas). É importante que a ordem de entrada dos dados corresponda entre os dois blocos.
No exemplo, vamos explorar a covariação entre a forma do crânio e a forma da mandíbula de roedores sigmodontíneos.
Carregar dados.
require(geomorph)
#> Le chargement a nécessité le package : geomorph
#> Le chargement a nécessité le package : RRPP
#> Le chargement a nécessité le package : rgl
#> Le chargement a nécessité le package : Matrix
# Carregar arquivo tps com a vista ventral do crânio
tps.v<-readland.tps("dadosmg/ventral.dig_curso.pls.tps",specID = "ID", readcurves = FALSE)
# Matriz com os pares de landmarks simétricos
pairs.matrix<-
matrix(c(2,3,4,5,6,7,8,9,10,11,12,13,14,15,16,17,18,24,22,28,23,29,19,25,20,26,21,27,30,31,33,34,35,36,37,38,39,40,41,42,43,44,45,46,47,48,49,50,51,52,55,56),nrow=26,ncol=2,byrow=T)
ind.v<-c(1:dim(tps.v)[3]) # vetor indivíduos
# GPA - Simetria bilateral - Extrair componente simetrico da forma
b.s<-bilat.symmetry(tps.v,ind=ind.v,object.sym=TRUE,land.pairs=pairs.matrix)
shape.v<-b.s$symm.shape # componente simétrico da forma
dimnames(shape.v)=dimnames(tps.v) #manter os nomes dos espécimes
shape.v
# Forma média ventral
ref.ventral<-mshape(shape.v)
# Carregar arquivo tps da mandíbula
tps<-readland.tps("dadosmg/mandibula.dig_curso.pls.tps",specID = "ID", readcurves = FALSE)
gpa<-gpagen(tps)
shape<-gpa$coords
size<-gpa$Csize
ref.mand<-mshape(shape)Carregar classificadores a partir de lista externa.
plan<-read.table("dadosmg/Planilha_PLS.txt",h=T)
plan
species.pls<-plan[,2]
species.plsPartial Least Squares - PLS.
pls<-two.b.pls(shape,shape.v,iter=999)
#>
#> Random PLS calculations: 1000 permutations.
#>
|
| | 0%
|
| | 1%
|
|= | 1%
|
|= | 2%
|
|= | 3%
|
|== | 3%
|
|== | 4%
|
|== | 5%
|
|=== | 5%
|
|=== | 6%
|
|=== | 7%
|
|==== | 7%
|
|==== | 8%
|
|==== | 9%
|
|===== | 9%
|
|===== | 10%
|
|===== | 11%
|
|====== | 11%
|
|====== | 12%
|
|====== | 13%
|
|======= | 13%
|
|======= | 14%
|
|======= | 15%
|
|======== | 15%
|
|======== | 16%
|
|======== | 17%
|
|========= | 17%
|
|========= | 18%
|
|========= | 19%
|
|========== | 19%
|
|========== | 20%
|
|========== | 21%
|
|=========== | 21%
|
|=========== | 22%
|
|=========== | 23%
|
|============ | 23%
|
|============ | 24%
|
|============ | 25%
|
|============= | 25%
|
|============= | 26%
|
|============= | 27%
|
|============== | 27%
|
|============== | 28%
|
|============== | 29%
|
|=============== | 29%
|
|=============== | 30%
|
|=============== | 31%
|
|================ | 31%
|
|================ | 32%
|
|================ | 33%
|
|================= | 33%
|
|================= | 34%
|
|================= | 35%
|
|================== | 35%
|
|================== | 36%
|
|================== | 37%
|
|=================== | 37%
|
|=================== | 38%
|
|=================== | 39%
|
|==================== | 39%
|
|==================== | 40%
|
|==================== | 41%
|
|===================== | 41%
|
|===================== | 42%
|
|===================== | 43%
|
|====================== | 43%
|
|====================== | 44%
|
|====================== | 45%
|
|======================= | 45%
|
|======================= | 46%
|
|======================= | 47%
|
|======================== | 47%
|
|======================== | 48%
|
|======================== | 49%
|
|========================= | 49%
|
|========================= | 50%
|
|========================= | 51%
|
|========================== | 51%
|
|========================== | 52%
|
|========================== | 53%
|
|=========================== | 53%
|
|=========================== | 54%
|
|=========================== | 55%
|
|============================ | 55%
|
|============================ | 56%
|
|============================ | 57%
|
|============================= | 57%
|
|============================= | 58%
|
|============================= | 59%
|
|============================== | 59%
|
|============================== | 60%
|
|============================== | 61%
|
|=============================== | 61%
|
|=============================== | 62%
|
|=============================== | 63%
|
|================================ | 63%
|
|================================ | 64%
|
|================================ | 65%
|
|================================= | 65%
|
|================================= | 66%
|
|================================= | 67%
|
|================================== | 67%
|
|================================== | 68%
|
|================================== | 69%
|
|=================================== | 69%
|
|=================================== | 70%
|
|=================================== | 71%
|
|==================================== | 71%
|
|==================================== | 72%
|
|==================================== | 73%
|
|===================================== | 73%
|
|===================================== | 74%
|
|===================================== | 75%
|
|====================================== | 75%
|
|====================================== | 76%
|
|====================================== | 77%
|
|======================================= | 77%
|
|======================================= | 78%
|
|======================================= | 79%
|
|======================================== | 79%
|
|======================================== | 80%
|
|======================================== | 81%
|
|========================================= | 81%
|
|========================================= | 82%
|
|========================================= | 83%
|
|========================================== | 83%
|
|========================================== | 84%
|
|========================================== | 85%
|
|=========================================== | 85%
|
|=========================================== | 86%
|
|=========================================== | 87%
|
|============================================ | 87%
|
|============================================ | 88%
|
|============================================ | 89%
|
|============================================= | 89%
|
|============================================= | 90%
|
|============================================= | 91%
|
|============================================== | 91%
|
|============================================== | 92%
|
|============================================== | 93%
|
|=============================================== | 93%
|
|=============================================== | 94%
|
|=============================================== | 95%
|
|================================================ | 95%
|
|================================================ | 96%
|
|================================================ | 97%
|
|================================================= | 97%
|
|================================================= | 98%
|
|================================================= | 99%
|
|==================================================| 99%
|
|==================================================| 100%
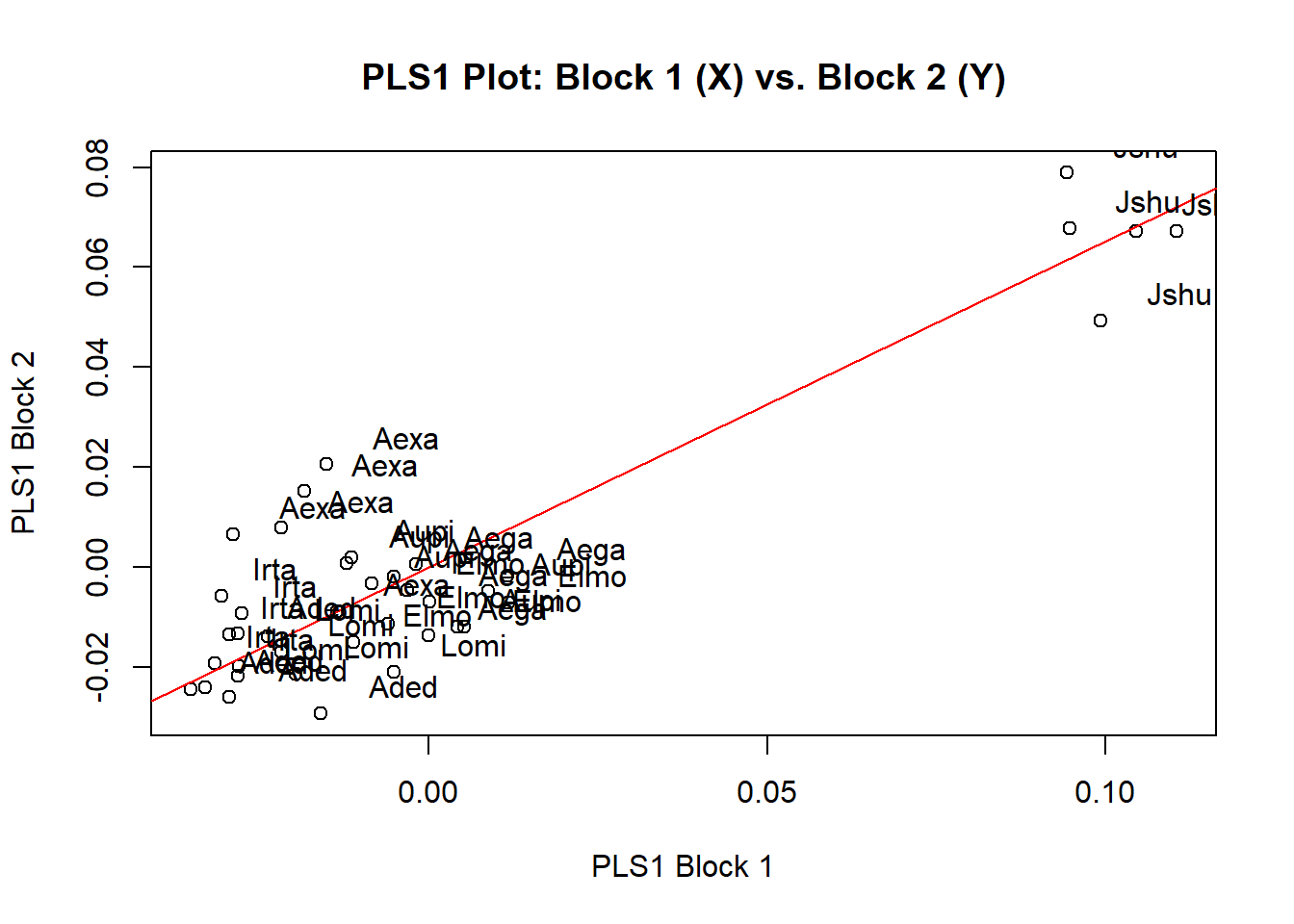
pls
#>
#> Call:
#> two.b.pls(A1 = shape, A2 = shape.v, iter = 999)
#>
#>
#>
#> r-PLS: 0.897
#>
#> Effect Size (Z): 4.257
#>
#> P-value: 0.001
#>
#> Based on 1000 random permutations
plot(pls,label=species.pls)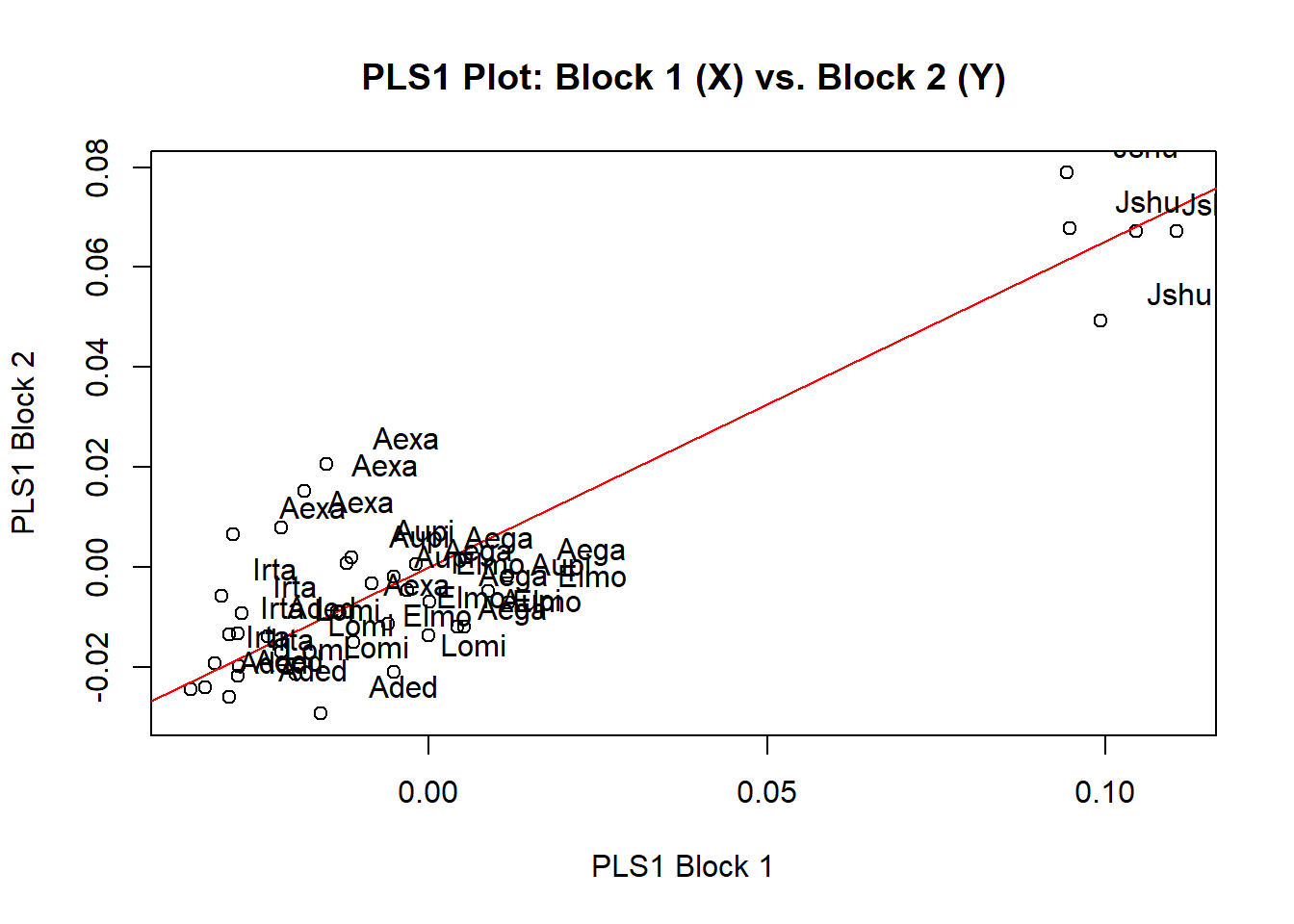
É possível visualizar as mudanças de forma ao longo dos eixos da PLS de diferentes maneiras. Uma delas é usando uma função interativa do pacote geomorph
pls.plot<-plot(pls)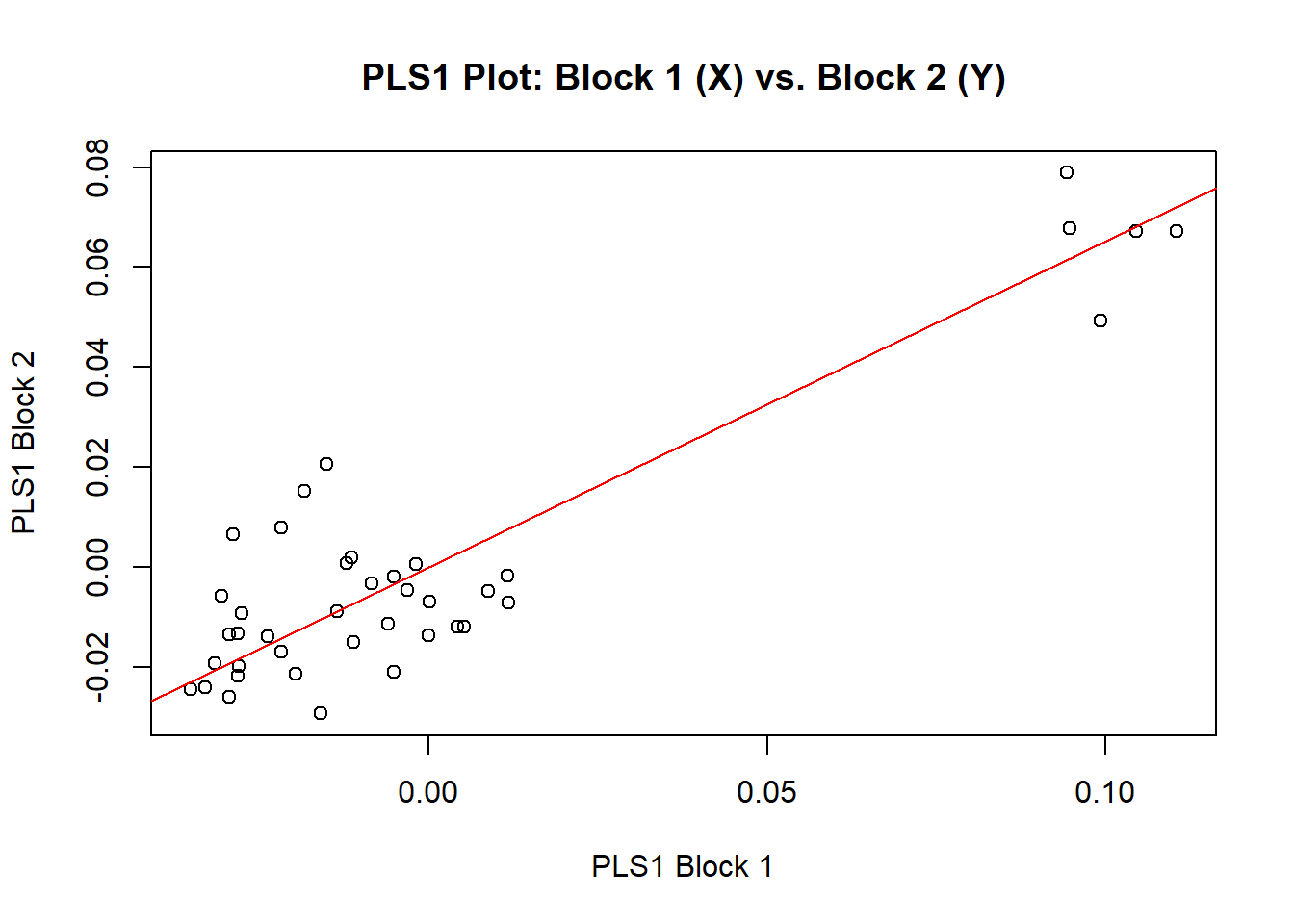
#picknplot.shape(pls.plot)A maneira mais tradicional é encontrar as formas a partir dos valores nos eixos da PLS.
pls<-two.b.pls(shape,shape.v,iter=999)
plot(pls,label=species.pls)
# Valores mínimos e máximos do pls plot
preds.v<-shape.predictor(shape.v,two.d.array(shape),method="PLS",
Vmin=min(pls$XScores[,1]),
Vmax=max(pls$XScores[,1]))
preds.v
# Valores mínimos e máximos do pls2
pls2<-two.b.pls(shape.v,shape,iter=999)
plot(pls2,label=species.pls)
preds.m<-shape.predictor(shape,two.d.array(shape.v),method="PLS",
Mmin=min(pls2$XScores[,1]),
Mmax=max(pls2$XScores[,1]))
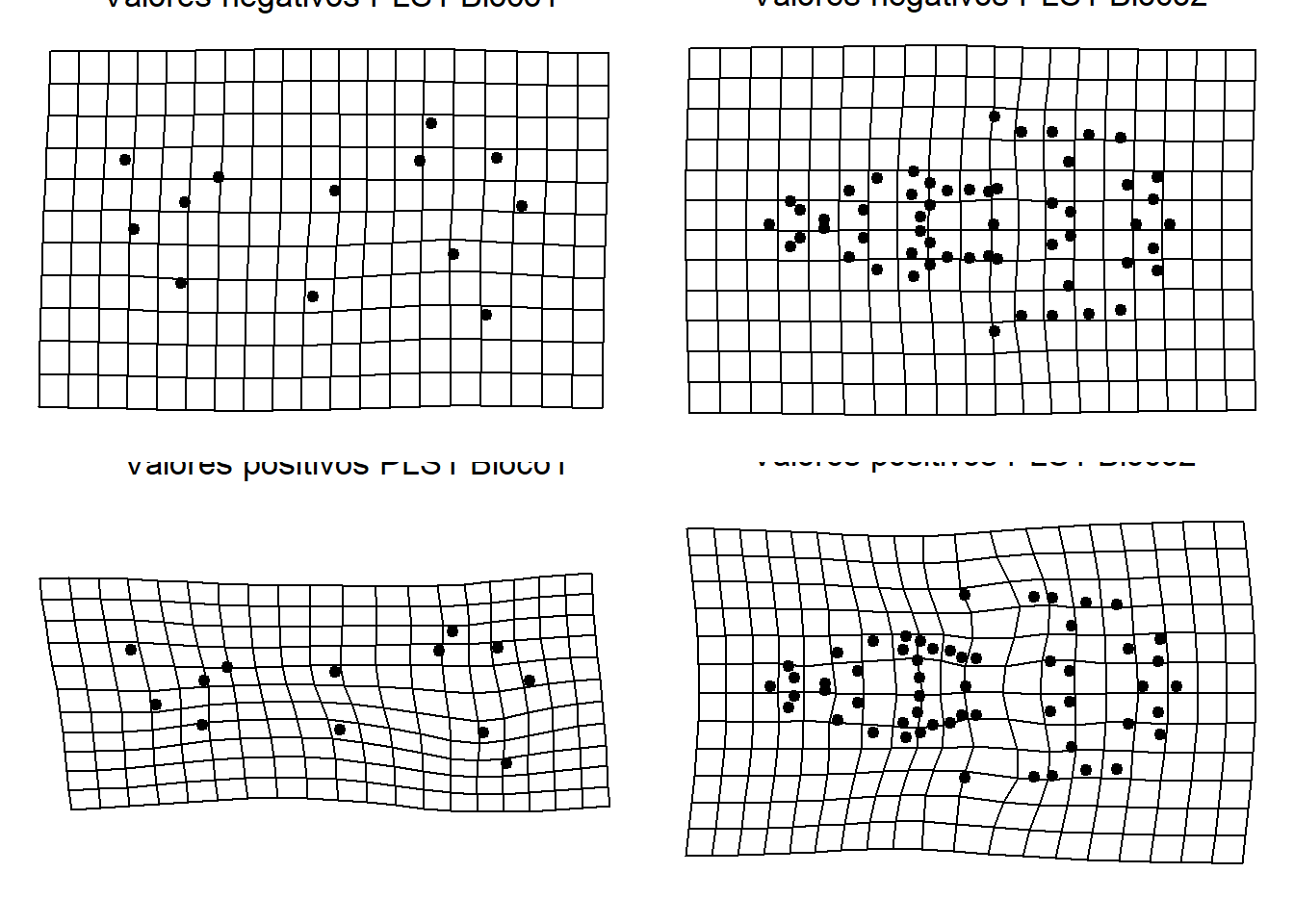
preds.mVisualização das formas mínimas e máximas dos eixos da PLS.
{plot(pls,label=species.pls)
par(mfrow=c(2,2),mar=c(0.01,0.01,0.01,0.01))
plotRefToTarget(ref.mand,preds.m$Mmax)
text(0,0.4,labels="Valores negativos PLS1 Bloco1",cex=1.3)
plotRefToTarget(ref.ventral,preds.v$Vmin)
text(0,0.25,labels="Valores negativos PLS1 Bloco2",cex=1.3)
plotRefToTarget(ref.mand,preds.m$Mmin)
text(0,0.4,labels="Valores positivos PLS1 Bloco1",cex=1.3)
plotRefToTarget(ref.ventral,preds.v$Vmax)
text(0,0.25,labels="Valores positivos PLS1 Bloco2",cex=1.3)}