Capítulo 17 Morfometria geométrica e filogenias
Quando as morfologias são de espécies diferentes, os dados não são independentes, já que as espécies são conectadas por uma árvore filogenética. A não-independência filogenética precisa ser levada em consideração em análises de correlação. Pra além disso, podemos entender muito sobre padrões e processos evolutivos da morfologia quando temos dados morfológicos de diferentes espécies e hipóteses filogenéticas. A parte deste manual sobre Macroevolução explora muitas perguntas/análises que podem ser feitas em um contexto comparativo. Aqui, os exemplos vão apresentar algumas análises comparativas no contexto de morfometria geométrica.
Para textos abrangentes sobre macroevolução e métodos filogenéticos comparativos no contexto de morfometria geométrica, veja: (zelditch2012?); (monteiro2013?); (adams&collyer2018?).
Para literatura geral, e muitas outras opções analíticas, veja o material e as referências na parte sobre Macroevolução deste manual.
Vamos carregar dados morfológicos obtidos por morfometria geométrica e uma hipótese filogenética para explorar algumas análises filogenéticas comparativas.
require(geomorph)
#> Le chargement a nécessité le package : geomorph
#> Le chargement a nécessité le package : RRPP
#> Le chargement a nécessité le package : rgl
#> Le chargement a nécessité le package : Matrix
# Carregar dados de forma média por espécie em formato de matriz
tps<-readland.tps("dadosmg/mandibula.dig_curso.pls.tps",specID = "ID", readcurves = FALSE)
gpa<-gpagen(tps)
shape<-gpa$coords
size<-gpa$Csize
ref.mand<-mshape(shape)
# Carregar classificadores a partir de lista externa
plan<-read.table("dadosmg/Planilha_PLS.txt",h=T)
plan
species<-as.factor(plan[,2])
species
# Calcular forma média por espécie
shape.2d<-two.d.array(shape)
shape.2d.means<-rowsum(shape.2d,species)/as.vector(table(species))
shape.means<-arrayspecs(shape.2d.means,dim(shape)[1],dim(shape)[2])
size.means<-rowsum(size,species)/as.vector(table(species))Hipótese filogenética.
require(ape)
#> Le chargement a nécessité le package : ape
tree<-read.nexus("dadosmg/nexus.tree.sig.nex")
plot(tree)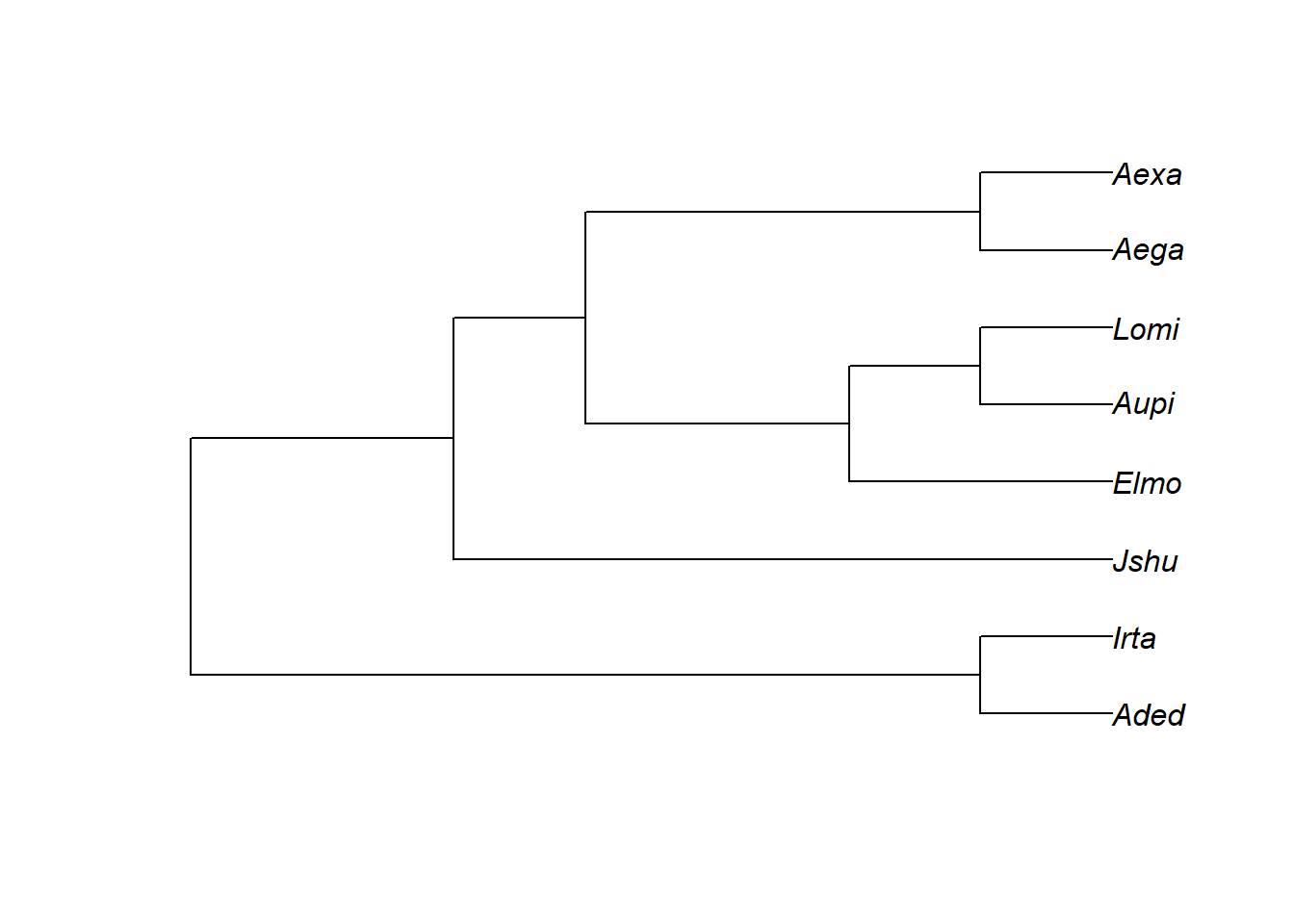
tree<-compute.brlen(tree,1) # definir comprimento dos ramos = 117.1 Filomorfoespaço
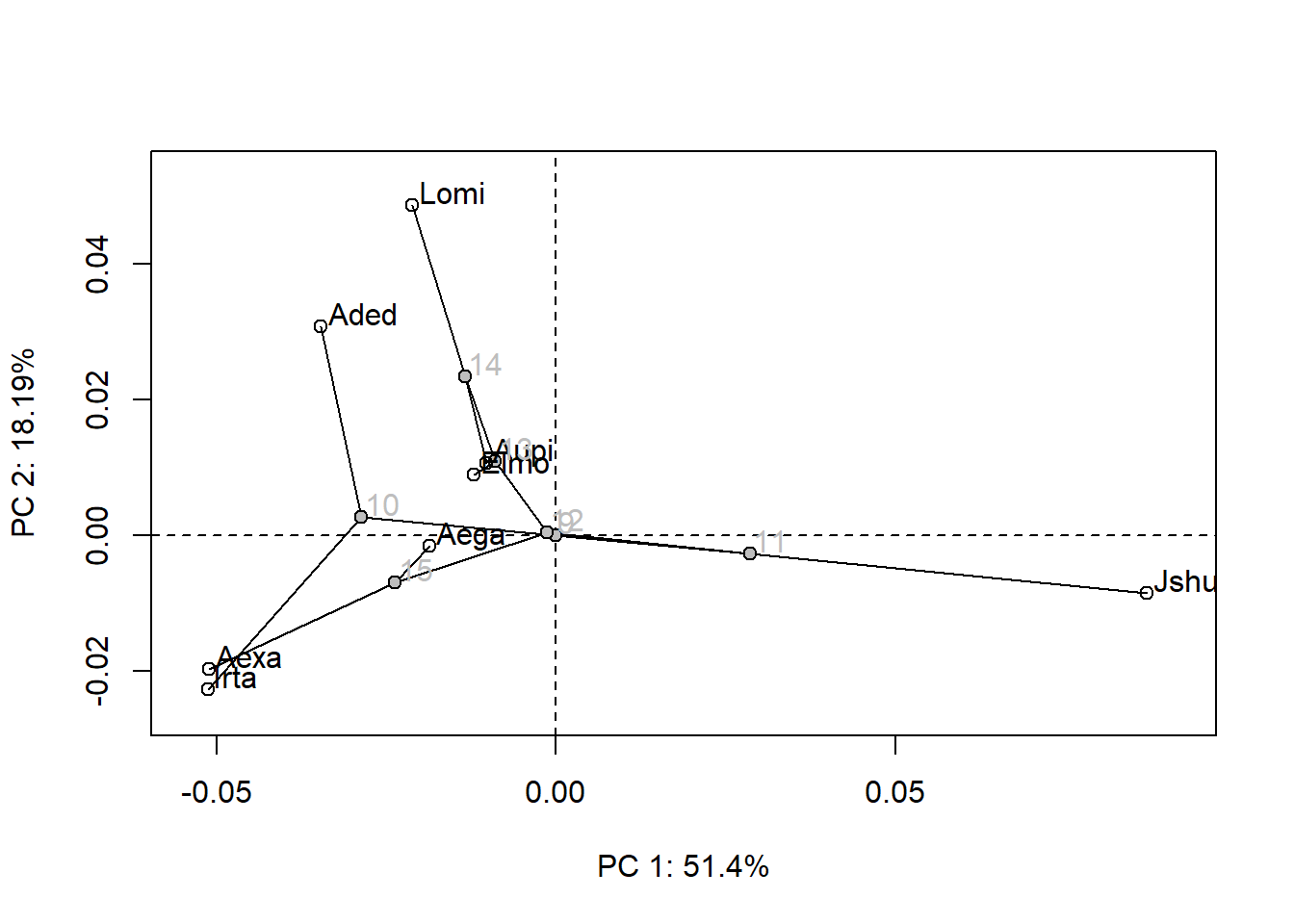
Podemos representar de maneira gráfica a filogenia no espaço de forma criado com uma análise de componentes principais. Essa é a PCA padrão, inalterada, com a projeção da filogenia e estimativa de formas ancestrais.
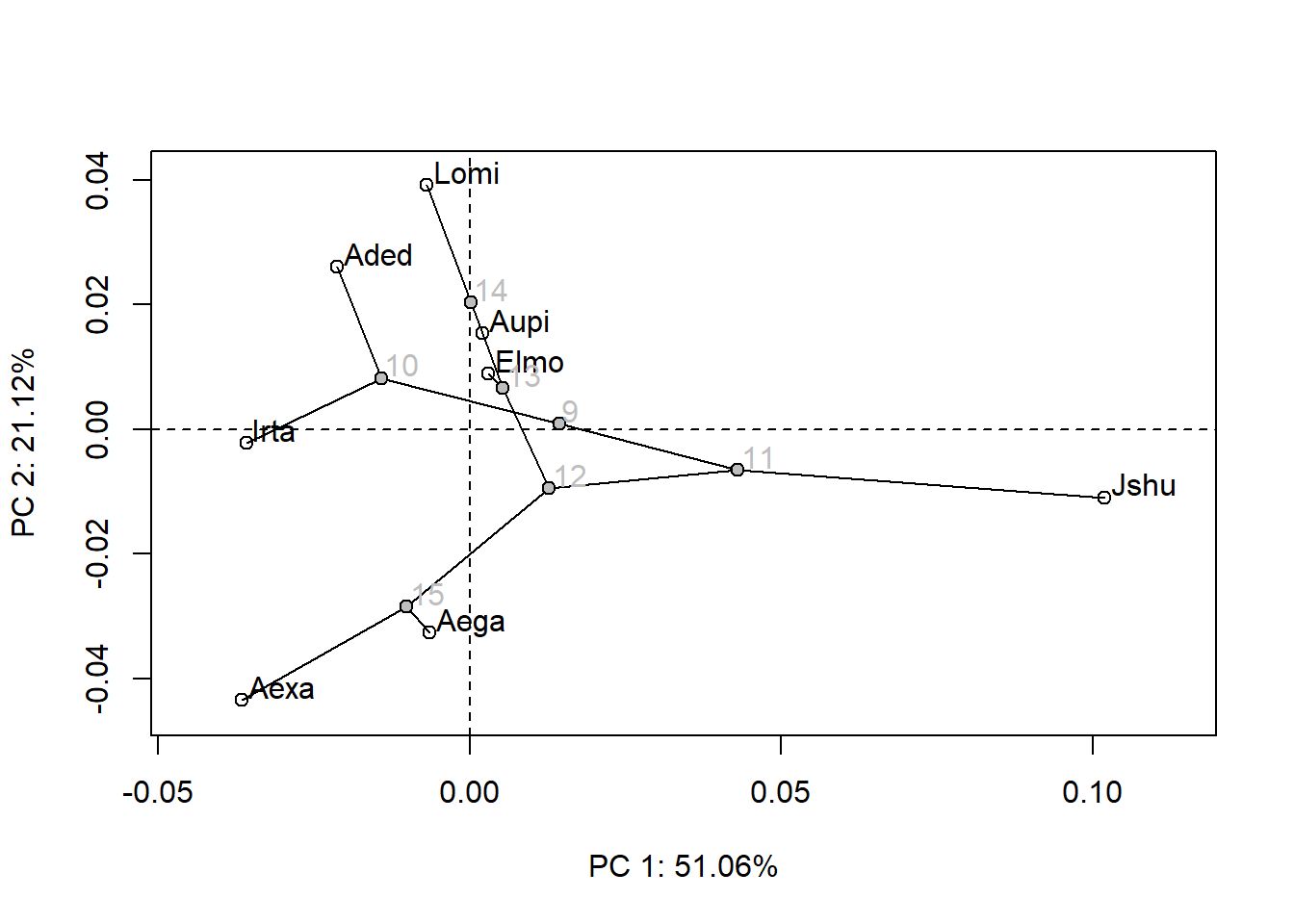
Filomorfoespaço 3D.
require(phytools)
#> Le chargement a nécessité le package : phytools
#> Le chargement a nécessité le package : maps
#phylomorphospace3d(tree,PCA$x[,1:3])A visualização de formas pode ser feita ao longo dos eixos, como na PCA tradicional, bem como podem ser visualizadas as formas ancestrais estimadas, formas médias de espécies atuais, etc.
ref<-mshape(shape.means)
ancestral.shapes<-arrayspecs(PCA$ancestors,13,2)
# Forma ancestral contra a média
plotRefToTarget(ref,ancestral.shapes[,,1],method="TPS")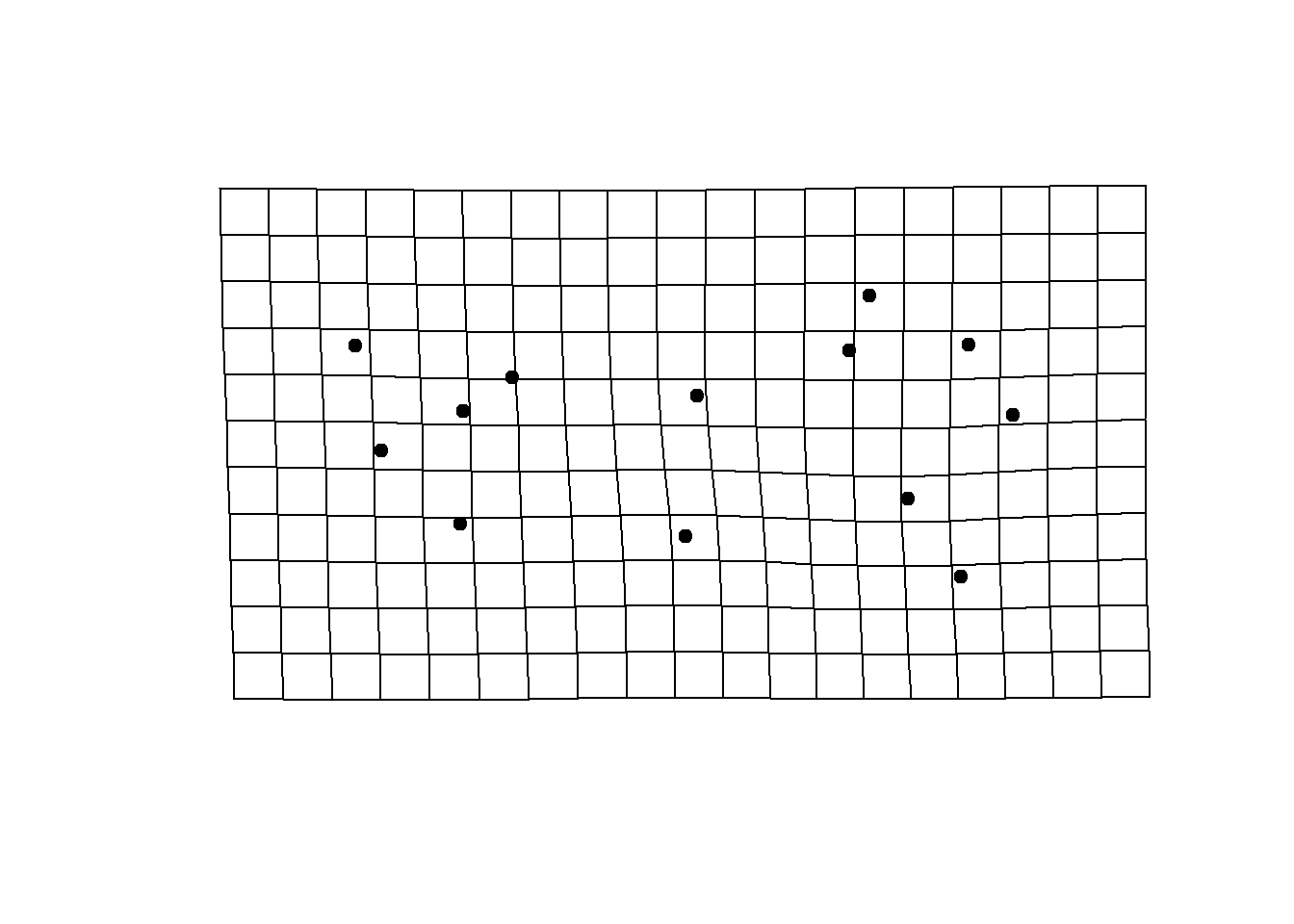
# Forma ancestral contra espécie atual
plotRefToTarget(ancestral.shapes[,,1],shape.means[,,"Aexa"],method="TPS")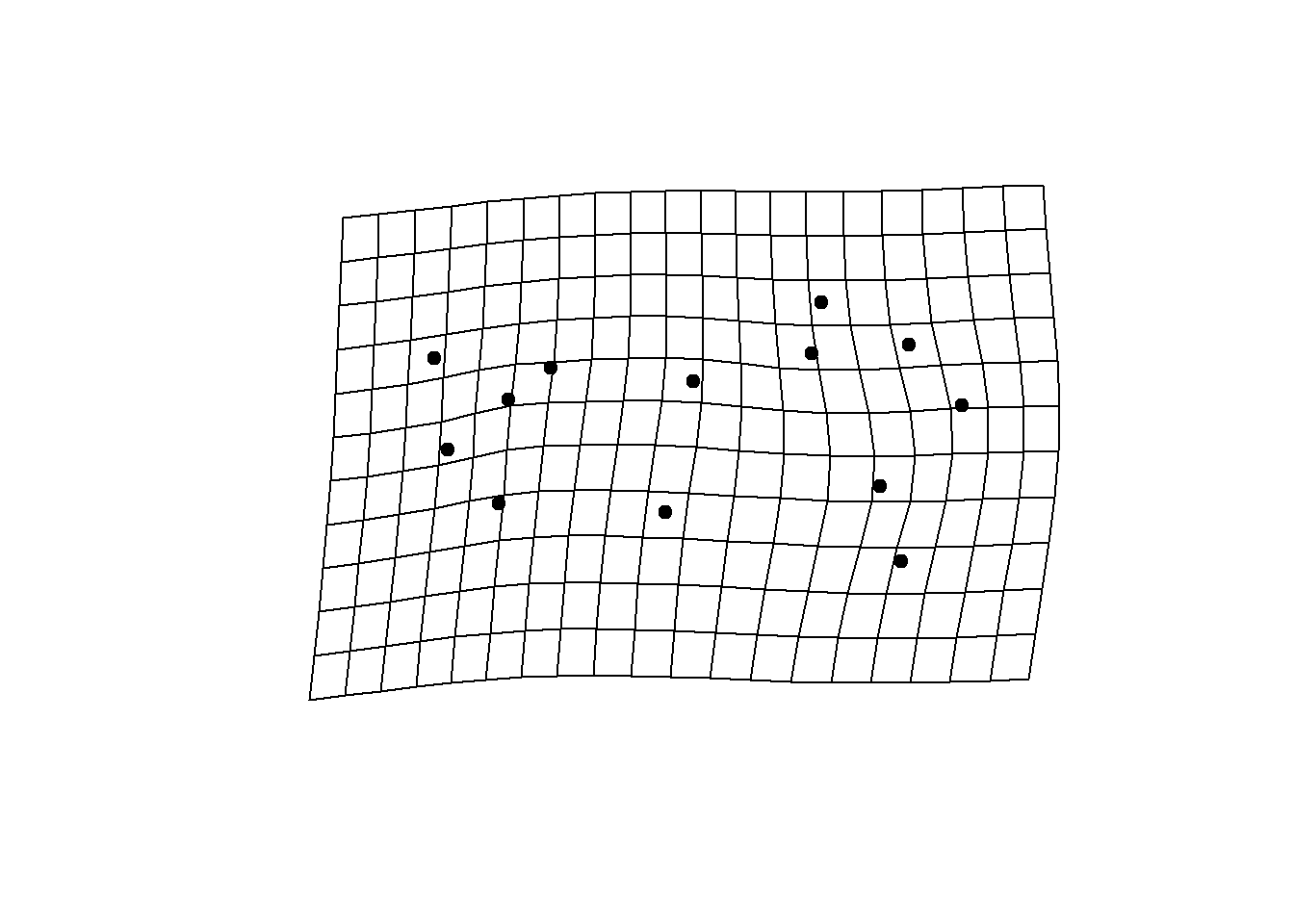
Visualizar tamanho ao longo da filogenia.
size.means1<-as.vector(size.means)
names(size.means1)=rownames(size.means)
tree1<-compute.brlen(tree,method="Grafen") # make ultrametric
# cores
contMap(tree1,size.means1)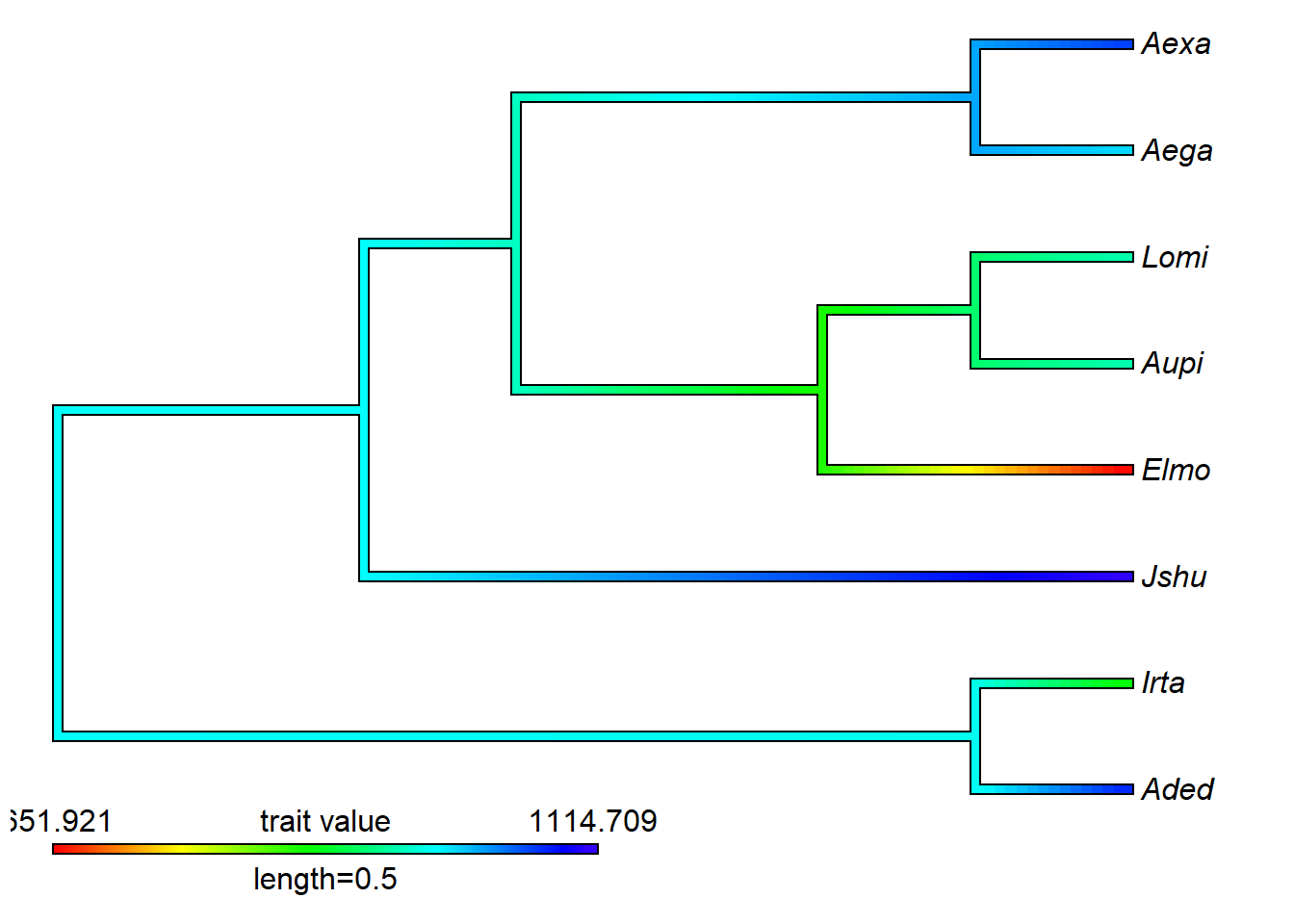
# dots
dotTree(tree1,size.means1,length=10)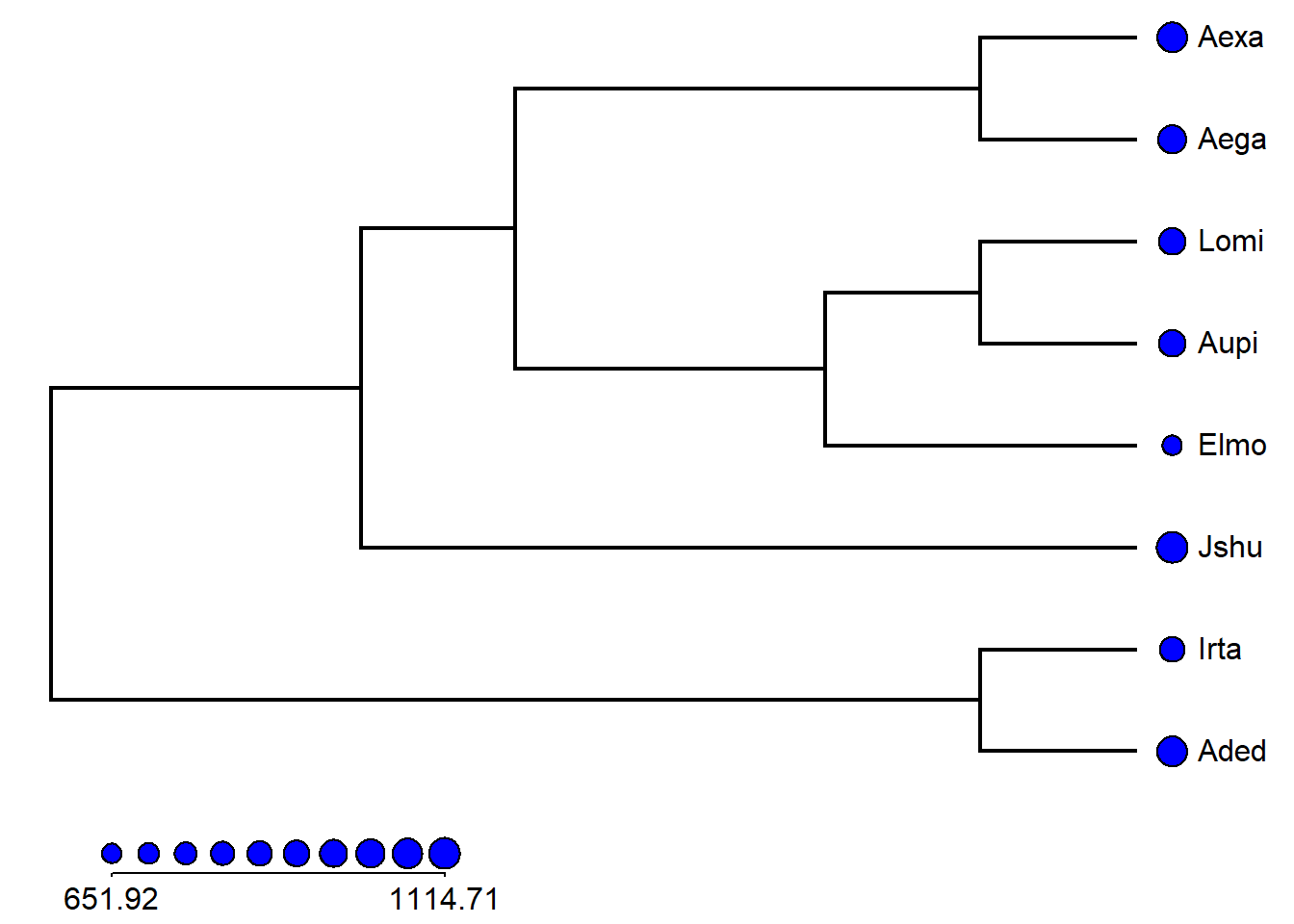
# barras
plotTree.barplot(tree1,size.means1)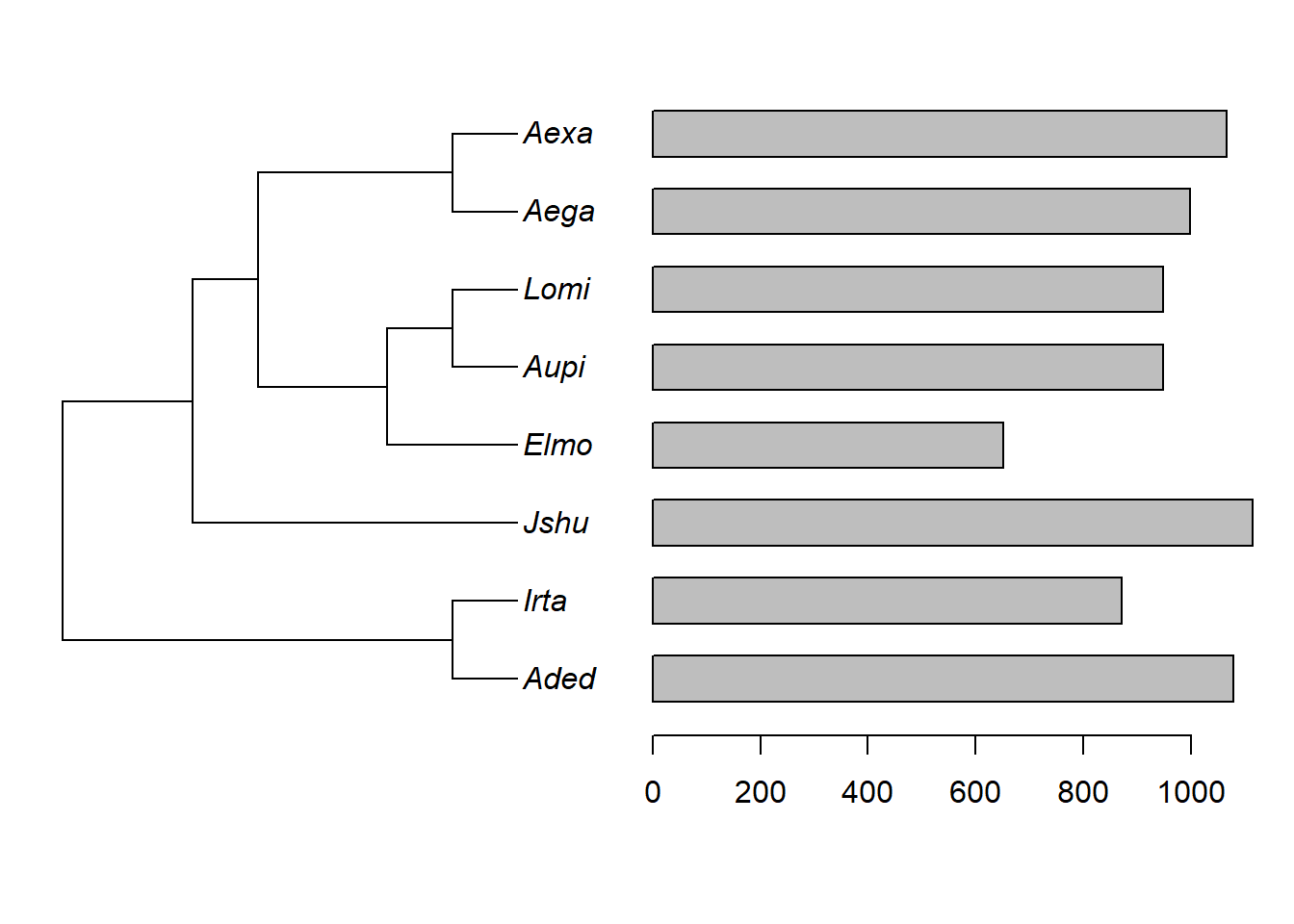
17.3 Sinal filogenético multivariado
Sinal filogenético é um padrão que mostra se espécies mais próximas filogeneticamente têm morfologias mais similares do que espécies mais distantes filogeneticamente. Existem vários métodos para o cálculo de sinal filogenético, o mais comum é a estatística K (Blomberg, Garland JR., and Ives 2003; adams2014?). K=1 indica que espécies próximas são tão parecidas quanto prevê o modelo Browniano K<1 indica sinal filogenético menor do que esperado pelo modelo Browniano K>1 indica sinal filogenético maior do que esperado pelo modelo Browniano
# Sinal Filogenético para forma do crânio
sinal.k<-physignal(shape.means,tree,iter=999)
sinal.k
#>
#> Call:
#> physignal(A = shape.means, phy = tree, iter = 999)
#>
#>
#>
#> Observed Phylogenetic Signal (K): 0.6146
#>
#> P-value: 0.158
#>
#> Based on 1000 random permutations
#>
#> Use physignal.z to estimate effect size.
# Sinal Filogenético para tamanho do crânio
sinal.k.size<-physignal(size.means,tree,iter=999)
sinal.k.size
#>
#> Call:
#> physignal(A = size.means, phy = tree, iter = 999)
#>
#>
#>
#> Observed Phylogenetic Signal (K): 0.5612
#>
#> P-value: 0.416
#>
#> Based on 1000 random permutations
#>
#> Use physignal.z to estimate effect size.17.4 Análise filogenética generalizada por quadrados mínimos (PGLS multivariada)
# Variáveis hipotéticas para usar como exemplo
nomes<-c("Aded","Aega","Aexa","Aupi","Elmo","Irta","Jshu","Lomi")
temp<-c(12.15,22,16.02,10.42,8.21,8.39,25,7.86)
alt<-c(2951,300,1931,3222,753.96,719.94,700,866.65)
names(temp)<-nomes
names(alt)<-nomes
gdf<-geomorph.data.frame(shape.means=shape.means,temp=temp,tree=tree)
fit.pgls<-procD.pgls(shape.means~temp,tree,data=gdf)
#>
#> Please be aware that printing progress slows down the analysis (perhaps slightly).
#>
#> Preliminary Model Fit...
#>
#> Sums of Squares calculations: 1000 permutations.
#>
|
| | 0%
|
| | 1%
|
|= | 1%
|
|= | 2%
|
|= | 3%
|
|== | 3%
|
|== | 4%
|
|== | 5%
|
|=== | 5%
|
|=== | 6%
|
|=== | 7%
|
|==== | 7%
|
|==== | 8%
|
|==== | 9%
|
|===== | 9%
|
|===== | 10%
|
|===== | 11%
|
|====== | 11%
|
|====== | 12%
|
|====== | 13%
|
|======= | 13%
|
|======= | 14%
|
|======= | 15%
|
|======== | 15%
|
|======== | 16%
|
|======== | 17%
|
|========= | 17%
|
|========= | 18%
|
|========= | 19%
|
|========== | 19%
|
|========== | 20%
|
|========== | 21%
|
|=========== | 21%
|
|=========== | 22%
|
|=========== | 23%
|
|============ | 23%
|
|============ | 24%
|
|============ | 25%
|
|============= | 25%
|
|============= | 26%
|
|============= | 27%
|
|============== | 27%
|
|============== | 28%
|
|============== | 29%
|
|=============== | 29%
|
|=============== | 30%
|
|=============== | 31%
|
|================ | 31%
|
|================ | 32%
|
|================ | 33%
|
|================= | 33%
|
|================= | 34%
|
|================= | 35%
|
|================== | 35%
|
|================== | 36%
|
|================== | 37%
|
|=================== | 37%
|
|=================== | 38%
|
|=================== | 39%
|
|==================== | 39%
|
|==================== | 40%
|
|==================== | 41%
|
|===================== | 41%
|
|===================== | 42%
|
|===================== | 43%
|
|====================== | 43%
|
|====================== | 44%
|
|====================== | 45%
|
|======================= | 45%
|
|======================= | 46%
|
|======================= | 47%
|
|======================== | 47%
|
|======================== | 48%
|
|======================== | 49%
|
|========================= | 49%
|
|========================= | 50%
|
|========================= | 51%
|
|========================== | 51%
|
|========================== | 52%
|
|========================== | 53%
|
|=========================== | 53%
|
|=========================== | 54%
|
|=========================== | 55%
|
|============================ | 55%
|
|============================ | 56%
|
|============================ | 57%
|
|============================= | 57%
|
|============================= | 58%
|
|============================= | 59%
|
|============================== | 59%
|
|============================== | 60%
|
|============================== | 61%
|
|=============================== | 61%
|
|=============================== | 62%
|
|=============================== | 63%
|
|================================ | 63%
|
|================================ | 64%
|
|================================ | 65%
|
|================================= | 65%
|
|================================= | 66%
|
|================================= | 67%
|
|================================== | 67%
|
|================================== | 68%
|
|================================== | 69%
|
|=================================== | 69%
|
|=================================== | 70%
|
|=================================== | 71%
|
|==================================== | 71%
|
|==================================== | 72%
|
|==================================== | 73%
|
|===================================== | 73%
|
|===================================== | 74%
|
|===================================== | 75%
|
|====================================== | 75%
|
|====================================== | 76%
|
|====================================== | 77%
|
|======================================= | 77%
|
|======================================= | 78%
|
|======================================= | 79%
|
|======================================== | 79%
|
|======================================== | 80%
|
|======================================== | 81%
|
|========================================= | 81%
|
|========================================= | 82%
|
|========================================= | 83%
|
|========================================== | 83%
|
|========================================== | 84%
|
|========================================== | 85%
|
|=========================================== | 85%
|
|=========================================== | 86%
|
|=========================================== | 87%
|
|============================================ | 87%
|
|============================================ | 88%
|
|============================================ | 89%
|
|============================================= | 89%
|
|============================================= | 90%
|
|============================================= | 91%
|
|============================================== | 91%
|
|============================================== | 92%
|
|============================================== | 93%
|
|=============================================== | 93%
|
|=============================================== | 94%
|
|=============================================== | 95%
|
|================================================ | 95%
|
|================================================ | 96%
|
|================================================ | 97%
|
|================================================= | 97%
|
|================================================= | 98%
|
|================================================= | 99%
|
|==================================================| 99%
|
|==================================================| 100%
summary(fit.pgls)
#>
#> Analysis of Variance, using Residual Randomization
#> Permutation procedure: Randomization of null model residuals
#> Number of permutations: 1000
#> Estimation method: Generalized Least-Squares (via OLS projection)
#> Sums of Squares and Cross-products: Type I
#> Effect sizes (Z) based on F distributions
#>
#> Df SS MS Rsq F Z
#> temp 1 0.072892 0.072892 0.26685 2.1839 0.93768
#> Residuals 6 0.200262 0.033377 0.73315
#> Total 7 0.273153
#> Pr(>F)
#> temp 0.202
#> Residuals
#> Total
#>
#> Call: procD.lm(f1 = shape.means ~ temp, iter = iter, seed = seed, RRPP = TRUE,
#> SS.type = SS.type, effect.type = effect.type, int.first = int.first,
#> Cov = Cov, data = data, print.progress = print.progress)17.5 Contrastes filogenéticos independentes
pic.size<-pic(size.means1,tree)
pic.temp<-pic(temp,tree)
fit.pic<-lm(pic.size~pic.temp+0) # regressão pela origem, a direção da subtração foi arbitrária no cálculo dos PICs
summary.aov(fit.pic) # mesmo resultado da PGLS
plot(pic.size~pic.temp)
17.6 Exercício - Morfometria e filogenias
Carregue o arquivo .tps ‘Roedores_Digitalizados.tps’ contendo coordenadas digitalizadas na mandíbula de 143 indivíduos de 19 espécies de roedores. Carregue também a informação taxonômica de cada indivíduo (‘Roedores_classificador.txt’), e uma hipótese filogenética para as 19 espécies (‘Roedores_tree_nexus.nex’). Existe um arquivo adicional que informa a força da mordida média de cada uma das 19 espécies (‘Roedores_BiteForce.txt’). Investigue a força do sinal filogenético para o tamanho e a forma do crânio, e descubra se existe relação entre a força da mordida e a forma (e tamanho) do crânio.